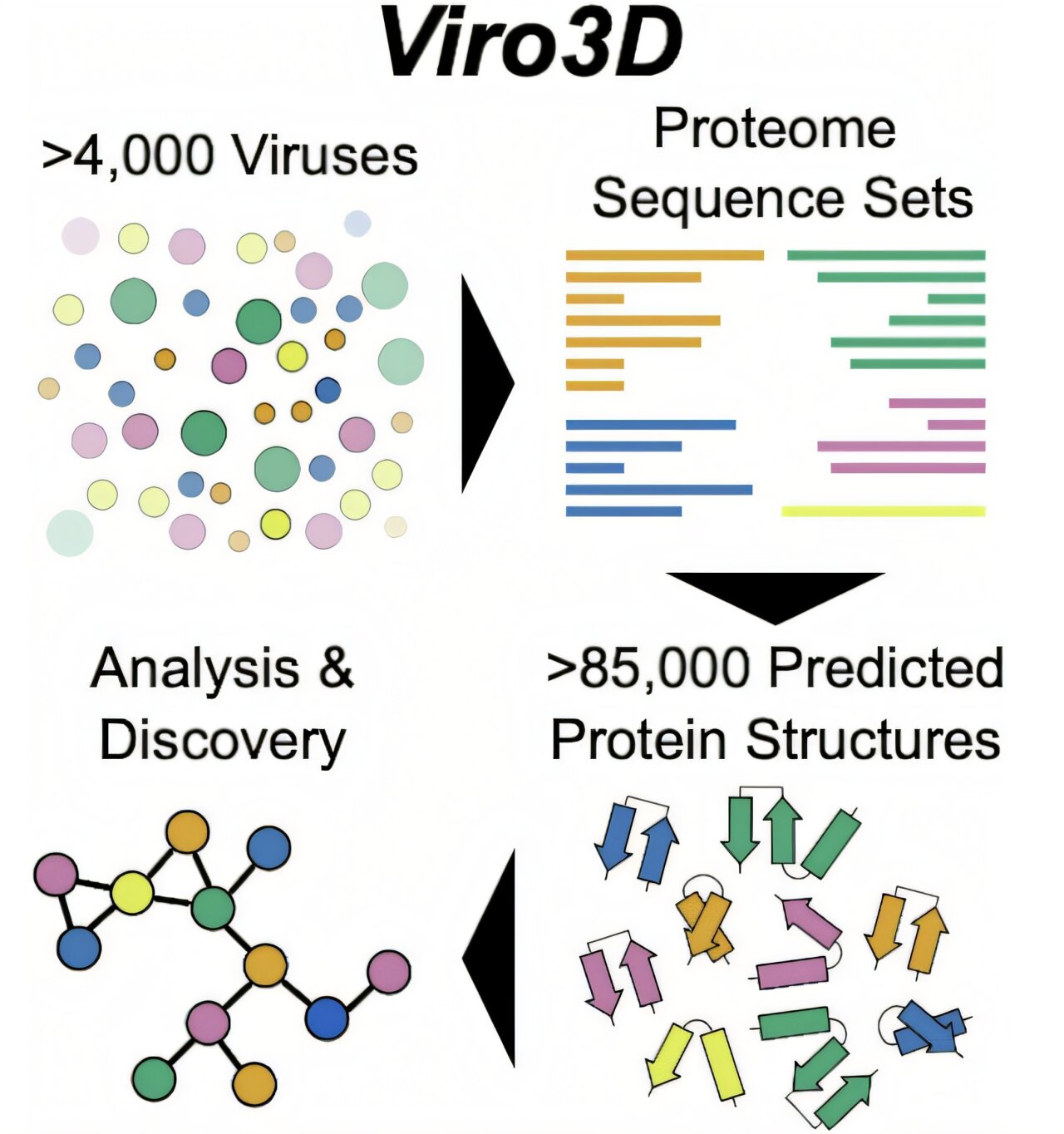
Exploitant le pouvoir de l’IA, une équipe de recherche de la MRC-University of Glasgow Center for Virus Research a lancé Viro3D – la base de données la plus complète des prédictions de la structure des protéines de virus humain et animal dans le monde.
La base de données gratuite et consultable alimentée par AI offre une perspective complètement nouvelle et approfondie sur les virus, ce qui nous permet d’en savoir plus sur leurs origines et leur évolution.
Bien que les particules virales soient les entités biologiques les plus abondantes de notre planète, ces minuscules structures restent parmi les moins bien compris. Des informations sur les principales structures protéiques au sein des virus n’ont, jusqu’à présent, été obtenu que par des travaux de recherche lents et laborieux, un rythme qui a eu un impact sur notre capacité à développer des traitements et des vaccins à grande vitesse.
Maintenant, dans un effort pour accélérer notre compréhension, une équipe de chercheurs, dirigée par le Dr Joe Grove dans le MRC-University of Glasgow Center for Virus Research, a exploité le pouvoir de l’IA pour créer une nouvelle base de données de milliers de protéines virales humaines et animales.
Viro3D contient des modèles structurels de haute qualité pour 85 000 protéines provenant de 4 400 virus humains et animaux – la plus grande base de données de modèles structurels complets pour les virus humains et animaux, élargissant nos connaissances actuelles dans ce domaine à 30 fois.
Les créateurs de Viro3d s’attendent à ce que la base de données commencera une nouvelle ère pour la recherche sur le virus humain et animal et accélère le développement de médicaments antiviraux et de vaccins contre les virus endémiques existants, tels que l’hépatite, le VIH, le rhume et le Covid-19 communs, ainsi que pour les menaces pandémiques nouvelles et émergentes.
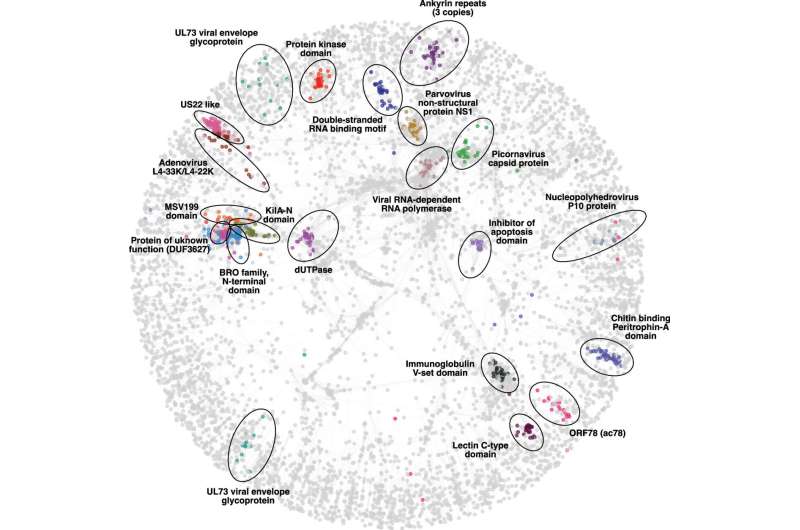
La base de données, qui a été récemment détaillée dans le journal Biologie des systèmes moléculairesa déjà révélé des informations auparavant inconnues sur l’ascendance génétique de SARS-COV-2, le virus responsable de Covid-19.
Les données de Viro3D suggèrent qu’une protéine clé dans SARS-CoV-2, l’une des responsables de l’infection, peut être à l’origine provenant d’un échange génétique avec un herpèsvirus ancestral, la famille des virus responsable d’une gamme de maladies, notamment des boutons de froid et de la variole.
L’équipe de recherche affirme que Viro3D a le potentiel de générer beaucoup plus d’informations comme celle-ci – sur l’histoire et les origines évolutives des virus – pour des milliers de protéines différentes, aidant à turbier notre compréhension des virus humains et animaux, et à leur tour notre capacité à les combattre au rythme.
Le Dr Joe Grove, auteur principal de la MRC-University of Glasgow Center for Virus Research, a déclaré: « Nous ne sommes qu’au début de la compréhension de l’énorme diversité génétique au sein de la communauté virale. Les virus sont aussi anciens que la vie cellulaire, ayant depuis des milliards d’années.
« Viro3d offre une toute nouvelle perspective sur les virus, nous permettant de découvrir leurs origines et leur évolution. Nous nous attendons à ce que Viro3D et l’intelligence artificielle accélèrent la conception informatique des médicaments antiviraux et des vaccins contre les virus endémiques existants. Nous pouvons ensuite ramener ces conceptions dans les laboratoires et ensuite au monde réel. »
Les protéines sont les éléments constitutifs de la vie, remplissant une vaste gamme de fonctions pour nos cellules et jouant un rôle critique à la fois dans la santé et la maladie. Afin de comprendre comment fonctionnent les protéines, les chercheurs doivent être en mesure d’examiner leur structure tridimensionnelle.
Alors que les progrès de l’intelligence artificielle ont conduit à la création de bases de données générales de structure des protéines, telles que la base de données Alphafold et l’atlas métagénomique de modélisation de l’échelle évolutive, les protéines virales ont jusqu’à présent été exclues des efforts de prédiction ou seulement inclus en petit nombre.